Forschung
Die Gruppe Crop Bioinformatics entwickelt und wendet Bioinformatik-Tools auf genomische Daten an, mit einem Fokus auf Nutzpflanzen. Wir sind Teil des Instituts für Nutzpflanzenwissenschaften und Ressourcenschutz an der Landwirtschaftlichen Fakultät der Universität Bonn und befinden uns zwischen den Fakultätsbüros und den Gewächshäusern in Poppelsdorf.
Insbesondere entwickeln wir Methoden zur Proteinfunktionsvorhersage und zur Analyse der Genfamilienevolution im Kontext adaptiver Prozesse. In Zusammenarbeit mit experimentellen Gruppen analysieren wir genomweite Expressionsdaten, Insertionsmutagenese-Datensätze und andere umfangreiche Sequenzierungsdaten.
Proteinfunktionsvorhersage


Gen-Funktionsbeziehungen
Die Verknüpfung phänotypischer Merkmale wie Wurzelwachstumswinkel oder Resistenz gegen bestimmte Umweltbelastungen mit kausalen Genen ist von zentraler Bedeutung für die Züchtung und Verbesserung von Pflanzen.
Dazu nutzen wir etablierte Ansätze (Transkriptomik, Bulked-Segregant-Analyse) und entwickeln neuartige bioinformatische Methoden wie Software für die automatische Analyse von Insertionsmutagenese-Bibliotheken und die In-silico-Vorhersage von Trait-assoziierten Genfamilien.
Genetische Marker
Molekulargenetische Marker sind eine Möglichkeit, Verwandtschaftsverhältnisse zwischen Arten, Populationen, Varianten oder sogar Individuen nachzuweisen. Daher erfordern unterschiedliche Analyseziele unterschiedliche Arten von genetischen Markern.
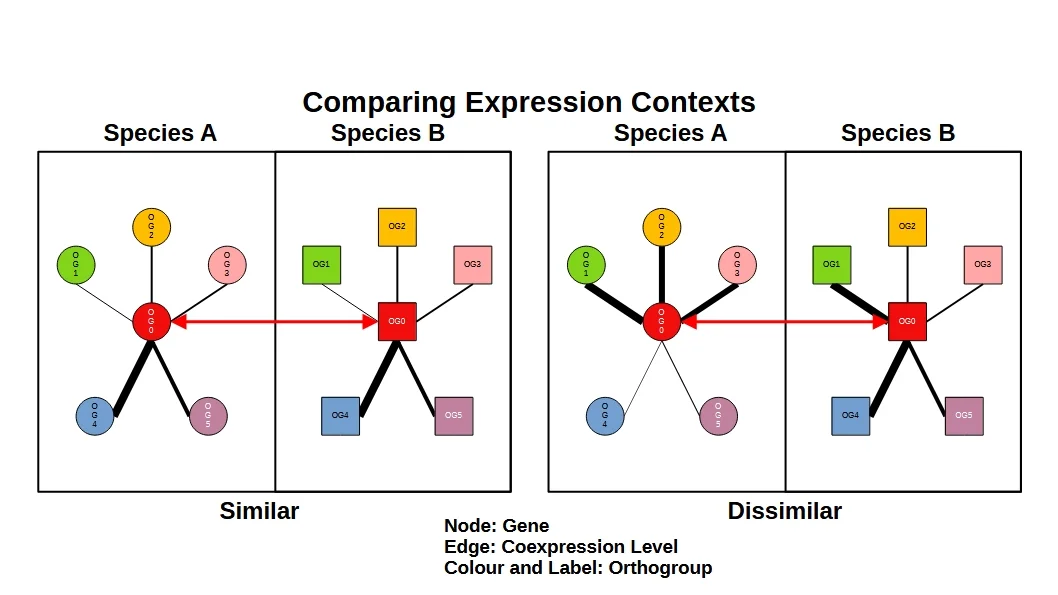
Evolution von Gen-Netzwerken
Viele Merkmale werden nicht ausschließlich durch einzelne Gene reguliert. Das Konzept der Genmodule die aus mehreren funktionell verwandten Genen bestehen, hat sich als nützlich erwiesen. Durch den Vergleich von Geninteraktionen zwischen verschiedenen Arten suchen wir nach Genmodulen, die funktionelle Innovationen und Anpassungen repräsentieren.